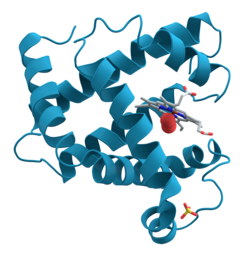
Ленточные диаграммы , также известные как диаграммы Ричардсона , представляют собой трехмерные схематические представления структуры белка и являются одним из наиболее распространенных методов изображения белков, используемых сегодня. Лента показывает общий путь и организацию белкового каркаса в 3D и служит визуальной рамкой, на которой можно вешать детали полной атомной структуры, такие как шары для атомов кислорода, связанных с активным участком миоглобина в соседнем изображение. Ленточные диаграммы генерируются путем интерполяции плавной кривой через основу полипептида . α-спирали показаны в виде свернутых лент или толстых трубок, β-тяжив виде стрелок и неповторяющихся витков или петель в виде линий или тонких трубок. Направление полипептидной цепи локально показано стрелками и может быть обозначено в целом шкалой цвета по длине ленты. [1]
Ленточные диаграммы просты, но эффективны, они отображают визуальные основы молекулярной структуры (скручивание, складывание и разворачивание). Этот метод успешно изобразил общую организацию белковых структур, отражая их трехмерную природу и позволяя лучше понять эти сложные объекты как опытным структурным биологам, так и другим ученым, студентам [2] и широкой публике.

История [ править ]
Первые ленточные диаграммы, нарисованные от руки Джейн С. Ричардсон в 1980 году (под влиянием более ранних отдельных иллюстраций) [3], были первыми схемами трехмерной структуры белка, которые производились систематически. [3] [4] Они были созданы, чтобы проиллюстрировать классификацию белковых структур для статьи в Advances in Protein Chemistry [5] (теперь доступны в аннотированной форме на сайте Anatax ). Эти рисунки были обведены пером на кальке поверх распечатки Cα- следа атомных координат и заштрихованы цветным карандашом или пастелью; [6]они сохранили позиции, сгладили магистральный путь и включили небольшие локальные сдвиги, чтобы устранить неоднозначность внешнего вида. [4] Помимо рисунка ленты триозоизомеразы справа, на других примерах, нарисованных от руки, изображены преальбумин , флаводоксин и Cu, Zn-супероксиддисмутаза .
В 1982 году Артур М. Леск и его сотрудники впервые включили автоматическое создание ленточных диаграмм с помощью вычислительной реализации, в которой в качестве входных данных используются файлы банка данных Protein . [7] Этот концептуально простой алгоритм подгоняет кубические полиномиальные B-сплайновые кривые к пептидным плоскостям. Большинство современных графических систем предоставляют либо B-шлицы, либо шлицы Эрмита.как базовый примитив чертежа. Один тип реализации сплайна проходит через каждую направляющую точку Cα, создавая точную, но прерывистую кривую. И нарисованные от руки, и большинство компьютерных лент (например, показанные здесь) сглаживаются примерно по четырем последовательным направляющим точкам (обычно по средней точке пептида), чтобы получить более визуально приятное и понятное изображение. Чтобы задать правильный радиус винтовой спирали при сохранении гладких β-нитей, шлицы можно модифицировать смещениями, пропорциональными локальной кривизне, как впервые разработал Майк Карсон для его программы Ribbons [8], а затем адаптировал с помощью другого программного обеспечения для молекулярной графики, такого как как программа Mage с открытым исходным кодом для графики kinemage [9], которая создавала изображение ленты вверху справа (другие примеры:Тример 1XK8 и ДНК-полимераза ).
С момента их создания и по настоящее время ленточные диаграммы были единственным наиболее распространенным представлением структуры белка и обычным выбором изображения обложки для журнала или учебника.
Текущие компьютерные программы [ править ]
Одна популярная программа, используемая для рисования ленточных диаграмм, - это Molscript . Molscript использует шлицы Hermite для создания координат витков, витков, нитей и спиралей. Кривая проходит через все свои контрольные точки ( атомы Cα ), ориентируясь по векторам направления. Программа была построена на основе традиционной молекулярной графики Артуром М. Леском , Карлом Хардманом и Джоном Пристлом. [10] Jmol - это программа просмотра на основе Java с открытым исходным кодом для просмотра молекулярных структур в сети; он включает упрощенную «мультяшную» версию лент. Другие графические программы, такие как DeepView (пример: уреаза ) и MolMol (пример: домен SH2 ), также создают ленточные изображения. Король[11] является Javaоснове преемником Mage (примеры: α-гемолизина вид сверху и вид сбоку ).
UCSF Chimera - это мощная программа молекулярного моделирования, которая также включает в себя визуализации, такие как ленты, примечательные особенно способностью комбинировать их с контурными формами из данных криоэлектронной микроскопии . [12] PyMOL , автор Warren DeLano , [13] - популярная и гибкая программа молекулярной графики (основанная на Python ), которая работает в интерактивном режиме, а также создает 2D-изображения презентационного качества для ленточных диаграмм и многих других представлений.
Особенности [ править ]
| Вторичная структура [4] [5] | |
|---|---|
| α-спирали | Цилиндрические спиральные ленты, плоскость которых приблизительно повторяет плоскость пептидов. |
| β-нити | Стрелки толщиной примерно в четверть их ширины показывают направление и изгиб нити от аминогруппы к карбоксильному концу. β-листы считаются едиными, потому что соседние нити скручиваются в унисон. |
| Петли и прочее | |
| Неповторяющиеся петли | Круглые веревки, которые толще на переднем плане и тоньше к спине, следуя сглаженной траектории следа Cα. |
| Переходы между петлями и спиралями | Круглая веревка, которая постепенно превращается в тонкую спиральную ленту. |
| Другие особенности | |
| Полипептидное направление, Концы NH 2 и COOH | Маленькие стрелки на одном или обоих концах или буквах. Для β-нитей достаточно направления стрелки. Сегодня направление полипептидной цепи часто указывается с помощью цветовой шкалы. |
| Дисульфидные связи | Переплетенный символ СС или зигзаг, похожий на стилизованный удар молнии. |
| Протезные группы или ингибиторы | Фигурки из палочек или мяч и клюшка . |
| Металлы | Сферы. |
| Затенение и цвет | Затенение или цвет добавляют диаграмме объемности. Как правило, элементы спереди наиболее контрастны, а элементы сзади - минимальны. |
См. Также [ править ]
- Молекулярная графика
Ссылки [ править ]
- ^ Смит, Томас Дж. (27 октября 2005 г.). «Отображение и анализ атомных структур на Macintosh» . Научный центр растений Данфорта. Архивировано из оригинального 28 марта 2002 года.
- ^ Ричардсон, округ Колумбия; Ричардсон, Дж. С. (январь 2002 г.). «Обучение молекулярной 3-D грамотности» . Биохимия и молекулярная биология образования . 30 (1): 21–26. DOI : 10.1002 / bmb.2002.494030010005 .
- ^ Б Ричардсон, Джейн С. (2000), "Ранние рисунки ленты белков", Nature Structural Biology , 7 (8): 624-625, DOI : 10.1038 / 77912 , PMID 10932243 .
- ^ Б с Ричардсон, Джейн S. (1985), "схематичные чертежи белковых структур" , Методы в энзимологии , методы в энзимологии, 115 : 359-380 , DOI : 10.1016 / 0076-6879 (85) 15026-3 , ISBN 978-0-12-182015-2, PMID 3853075.
- ^ Б Ричардсон, Джейн С. (1981), "Анатомия и таксономические белковые структуры", достижения в области химии белка , достижения в области химии белка, 34 : 167-339, DOI : 10.1016 / S0065-3233 (08) 60520-3 , ISBN 978-0-12-034234-1, PMID 7020376.
- ↑ «Мать ленточных диаграмм» Science отмечает 50-летие Герцога » . Истории герцога . 2018-10-19 . Проверено 9 июня 2020 .
- ^ Леск, Артур М .; Hardman, Карл Д. (1982), "Computer-Generated Принципиальные схемы белковых структур", Science , 216 (4545): 539-540, Bibcode : 1982Sci ... 216..539L , DOI : 10.1126 / science.7071602 , PMID 7071602 .
- ^ Карсон, М .; Bugg, CE (1986), "Алгоритм Ribbon моделей белков", журнал Molecular Graphics , 4 (2): 121-122, DOI : 10,1016 / 0263-7855 (86) 80010-8.
- ^ Ричардсон, округ Колумбия; Ричардсон, JS (январь 1992), "О kinemage: инструмент для научного общения", Protein Science , 1 (1): 3-9, DOI : 10.1002 / pro.5560010102 , PMC 2142077 , PMID 1304880
- ^ MolScript v2.1: О программе
- ^ Чен, В.Б .; Дэвис, И. В.; Ричардсон, округ Колумбия (2009), «KING (Kinemage, Next Generation): универсальная интерактивная программа молекулярной и научной визуализации», Protein Science , 18 (11): 2403–2409, doi : 10.1002 / pro.250 , PMC 2788294 , PMID 19768809
- ^ Годдард, Томас Д .; Хуанг, Конрад С.; Ferrin, Томас (2005), "Программное обеспечение Расширение UCSF Химера для интерактивной визуализации больших молекулярных ассамблей", структура , 13 (3): 473-482, DOI : 10.1016 / j.str.2005.01.006 , PMID 15766548 .
- ^ Брюнгер, Аксель Т .; Уэллс, Джеймс А. (2009), "Уоррен Л. Делано, 21 июня 1972-3 ноября 2009", Nature Structural & Molecular Biology , 16 (12): 1202-1203, DOI : 10.1038 / nsmb1209-1202 , PMID 19956203 .
| Викискладе есть медиафайлы по теме ленточных диаграмм . |